adf:reaxffcountbonds
这是本文档旧的修订版!
用python统计ReaxFF轨迹中的分子个数、特定的键的数目变化
Python脚本右键另存下载并解压 该脚本只能分析AMS2023版的ReaxFF输出轨迹文件*.results/ams.rkf。
运行方式:
- AMSjobs进入作业所在文件夹 → Help → Command-line → 打开命令行窗口输入sh回车(如果是Linux,本身就有命令行,直接打开命令行即可)
- 该脚本下载到某作业所在文件夹,与作业的*.resutls/同级
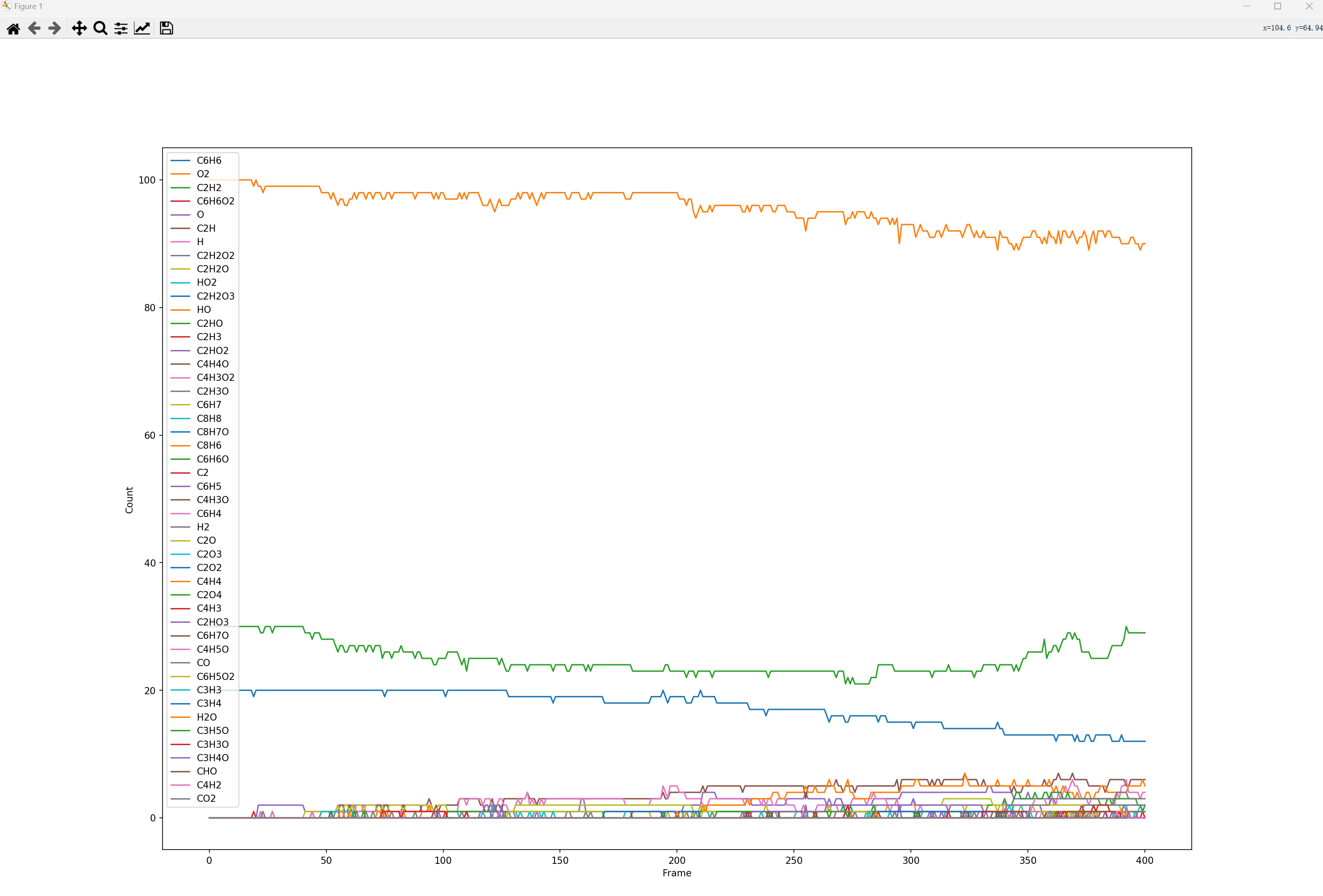
- 在命令行输入:amspython MoleculesTable.py test.results/ams.rkf回车。稍后将产生分子数列表窗口,可以关闭:
- 然后会弹出化学键数窗口,也可以关闭:
- 将生成:molecule_analysis.txt、molecule_analysis.pdf、bond_analysis.txt、bond_analysis.pdf四个文件。其中*.pdf文件是图,*.txt文件是曲线对应的数据,其中第一列为“帧”数,其他列为具体数据。
该脚本默认统计单、双、三键,如果需要统计芳香键,则修改脚本中:
round_type = 'integer' # round bond orders to nearest integer #round_type = 'half_integer' # round bond orders to nearest half integer
为
#round_type = 'integer' # round bond orders to nearest integer round_type = 'half_integer' # round bond orders to nearest half integer
注意
adf/reaxffcountbonds.1700649729.txt.gz · 最后更改: 2023/11/22 18:42 由 liu.jun